この記事はまだ書きかけです.
はじめに †
心電図のデータに対してRを用いて時系列解析を行う方法についてのメモです.
Rのインストールと基本的な使い方についてはこちらをご覧ください.
データの入手 †
あとで書きます.
時系列解析 †
準備 †
まず,データがあるディレクトリーに移動します. ここでは,デスクトップにあるECGディレクトリーとします.
> setwd("~/Desktop/ECG")
次に,ファイルを読み込みます. 今回のファイルはタブ区切りのファイルなので,区切り文字を\tとします.
> data <- read.csv("fig1.txt", header=FALSE, sep="\t")
このデータの列に名前を付けます.
> names(data) <- c("t", "x1", "x2")
2列目を時系列データとして取り出します.
> ecg <- ts(data$x1)
グラフ表示 †
時系列データを折れ線グラフとして描きます.
> plot(data$x1, type="l")
すると,次のようなグラフが描かれます.
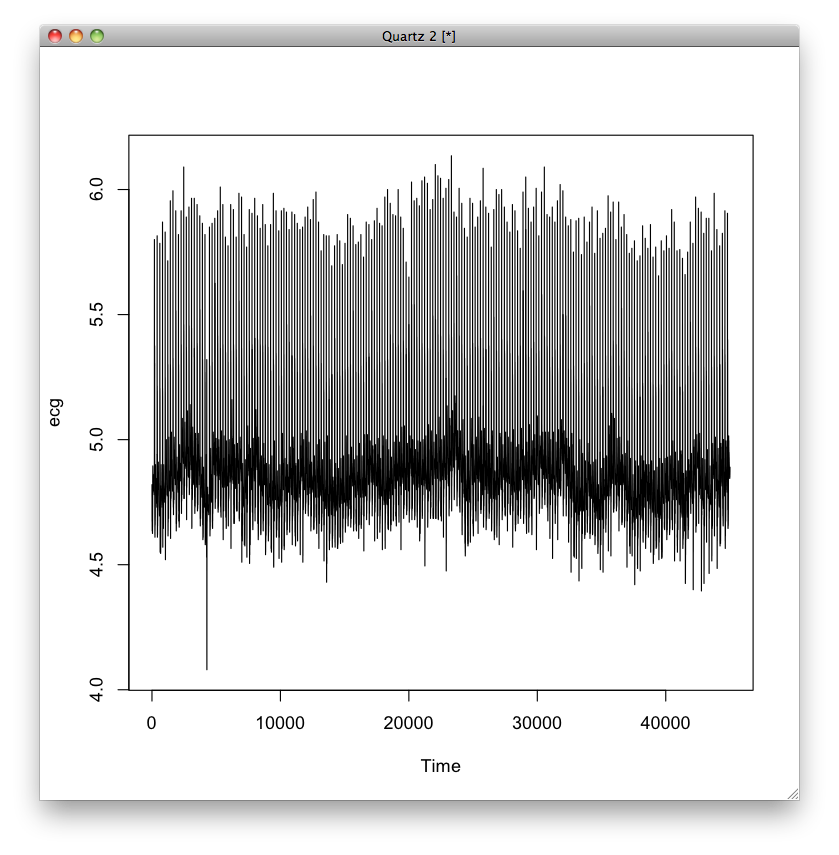
しかし,これではデータ数が多すぎて心電図のように見えませんので,表示する範囲を0から1000までに絞り込みます.
> plot(ecg,type="l",xlim=c(0,1000))
すると,次のようなグラフが描かれます.
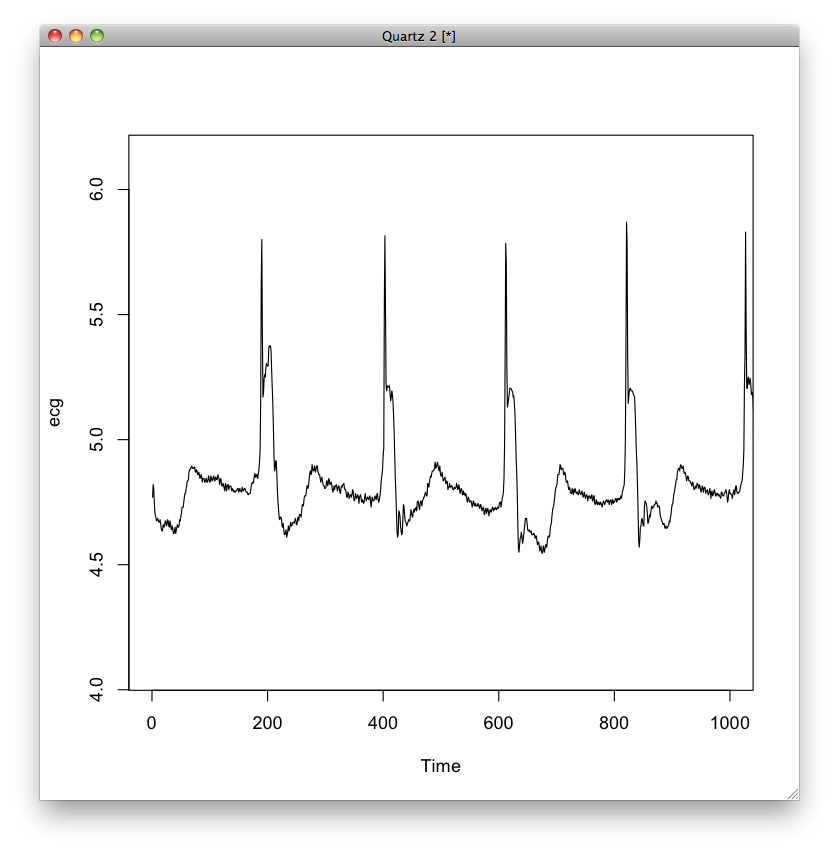
続きはまた今度.
![[PukiWiki] [PukiWiki]](https://xn--p8ja5bwe1i.jp:443/wiki/image/banner.png)